Teorias e métodos em melhoramento genético animal 3
Inicialização ao Melhoramento Genético de Produção Animal
1 Noções de genética quantitativa
Valor, Média e Variância
(em função das frequências gênica e genotípica)
valores
Os princípios genéticos relacionados com a herança dos caracteres quantitativos são basicamente aqueles da genética de populações, mas como a segregação dos genes não pode ser seguida individualmente, novos métodos de estudo são necessários e novos conceitos precisam ser introduzidos. Surge, assim, o ramo da genética quantitativa ou biométrica. A maioria dos caracteres de valor econômico são quantitativos e é nesse ramo que a genética tem a mais importante aplicação prática.
As propriedades genéticas de uma população podem ser expressas em termos de frequências gênica e genotípica. De modo a demonstrar a conecção entre as frequências gênica e genotípica, de um lado, e as diferenças quantitativas apresentadas por uma característica, de outro, introduz-se o conceito de “valor”, expresso na unidade métrica em que a característica é medida.
valores fenotípico,genotípico e ambiental
O valor observado quando a característica é medida em um indivíduo, é o “valor fenotípico”(P) desse indivíduo. Todos os parâmetros, como média, variância e covariância devem ser baseados nas medidas de valor fenotípico. Esse valor pode ser obtido para qualquer característica (peso ao nascer, peso à desmama, produção de leite/Lactação, espessura de toucinho etc).
Para a análise das propriedades genéticas da população, o valor fenotípico é
dividido em partes componentes atribuíveis a diferentes causas. A primeira divisão é nos componentes atribuíveis ao genótipo e ao meio ambiente. Genótipo refere-se ao conjunto de genes que cada indivíduo em particular possui. Ambiente é toda circunstância não genética que influencie o valor fenotípico. Os dois componentes de valor associados com o genótipo e o meio ambiente são: “valor genotípico” (G) e “desvios ambientais” (E)
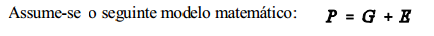
modelo genético
Sendo P = p - ìp , G = g - ìg e E = e - ìe . Esse modelo é conveniente porque o valor esperado (média) de cada elemento P, G ou E é zero e assim, os valores estimados para cada animal são expressos como + ou - o desvio em relação à média da população. Embora os caracteres quantitativos sejam determinados por vários loci, a segregação em cada locus não pode ser observada e a contribuição de cada gene não pode ser identificada. No entanto, os princípios da herança mendeliana se aplicam a cada locus, o mesmo ocorrendo com a ação gênica intra e interlocus. Assim, para introduzir o conceito de variação quantitativa, usa-se o modelo simples de herança, de um locus com dois alelos. O que importa é o desenvolvimento de modelos que descrevam os efeitos dos genes nas características de desempenho
valores genotípicos arbitrários(+a, d, -a)
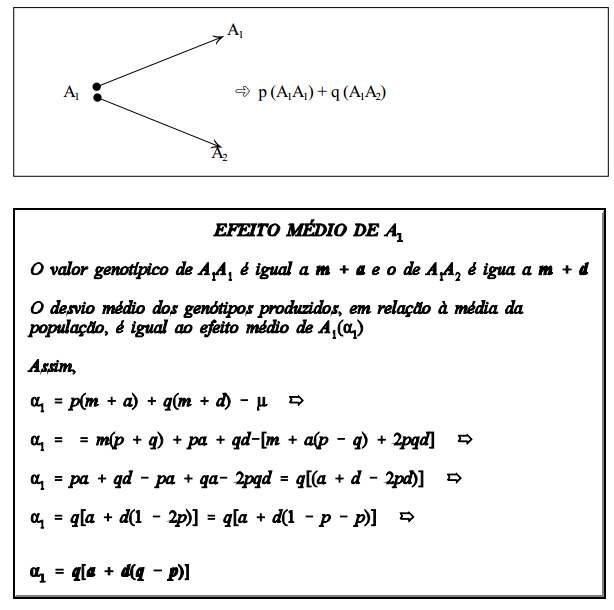
Como visto no capítulo de ação gênica e modelo genético, são atribuídos valores arbitrários aos genótipos sob discussão. Considerando-se um locus com dois alelos, A1 , A1 , designa-se por “+a” o valor genotípico de um homozigoto, “-a” o valor genotípico do outro homozigoto e “d” o valor genotípico do heterozigoto, dados como desvio da média dos valores genotípicos dos dois homozigotos. São, portanto, valores acima ou abaixo da média dos dois homozigotos. Esta média, ou ponto médio, é dada por:
Por convenção, A1 é o alelo que aumenta o valor. Tem-se, assim, uma escala de valores genotípicos (gráfico abaixo) em que a origem, ou ponto 0 (zero) é a média dos dois homozigotos (designada por m).
O valor d, do heterozigoto, depende do grau de dominância. Se não há dominância, d = 0; se A1 é dominante sobre A2 , d > 0; se A2 é dominante sobre A1 , d < 0. Se a dominância é completa, d = +a ou d = -a. Se ocorre sobredominância, d > +a ou d < -a. O grau de dominância pode ser expresso como d/a.
exemplo
Em camundongos, descreveu-se (Falconer, 1981) um gene recessivo, denominado "pigmeu" (pg), que reduz o tamanho corporal. Os pesos as seis semanas de idade (média dos dois sexos) de uma linhagem desses camundongos foram os seguintes:

Em princípio, o valor genotípico pode ser medido mas, na prática, isto não é
possível, exceto quando se trata de um único locus em que os genótipos são distinguíveis. No entanto, a média dos desvios ambientais de uma população como um todo é 0 (zero) e assim, o valor genotípico médio é igual ao valor fenotípico médio.

média da população
Sumponha-se que as frequências genotípicas sejam f(A1A1 ) = 0,81; f(A1A2 ) = 0,18 e f(A2A2 ) = 0,01.



2 Valor genotípico como desvio da média da população
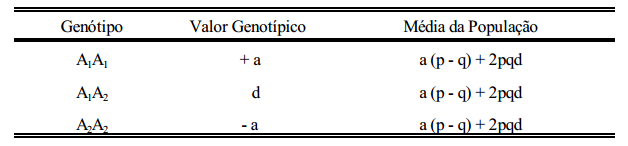
Trata-se do valor genotípico em função das frequências gênicas, dado como desvio da média da população. Considere-se o quadro abaixo:


conceito
De modo a demonstrar as propriedades de uma população em conexão com sua estrutura de família, deve-se pensar na transmissão do “valor”, de pai para descendente, o que não pode ser feito com base no “valor genotípico”, uma vez que um pai passa ao descendente seus genes e não seu genótipo. Em cada geração, novos genótipos são criados. Torna-se, assim, necessário uma nova medida que se refira aos genes e não aos genótipos. Isto possibilita a atribuição de um “valor genético” aos indivíduos, valor este, associado aos genes "transportados" pelo indivíduo e transmitido aos descendentes.
definição
O efeito médio de um gene é o desvio médio, em relação à média da população, de indivíduos que receberam o gene de um pai, sendo que o outro alelo (gene recebido do outro pai) veio ao acaso da população.
Considere-se, inicialmente, o efeito médio de A1 (á1 ). Suponha-se que determinado número de gametas "transportando" o gene A1 se una, ao acaso, a gametas da população. Na população, as frequências gênicas de A1 e de A2 , são respectivamente, p e q. A frequência genotípica dos descendentes será, então, igual a p(A1A1 ) + q (A1A2 ), como mostrado na figura abaixo.

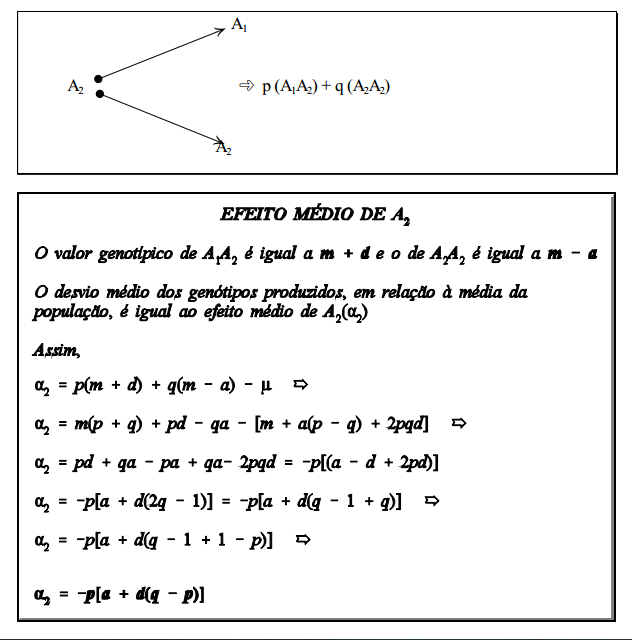
Considere-se, agora, o efeito médio do gene A2

efeito médio de substituição de um gene
É a mudança média que ocorre na média da população, quando se substitui um dos alelos pelo outro.
Considere-se á como sendo o efeito da substituição de A2 por A1
- Dos genes A2 tomados ao acaso da população, uma proporção p será encontrada nos genótipos A1A2 e uma proporção q, nos genótipos A2A2
-Tem-se assim,


valor genotípico (G) em função de a
Este valor genotípico é também dado como desvio da média da população, ou seja, o valor indica quanto o indivíduo com o referido genótipo é superior ou inferior à média da população.



3 Valor genético aditivo(A)
conceito
O efeito médio dos genes dos pais determina o valor genotípico médio de sua progênie, portanto, o valor genotípico médio de um determinado número de progênies, sob determinadas condições, determina o valor genético de um pai. Para isso, o reprodutor a ser avaliado deve ser acasalado com determinado número de fêmeas, tomadas ao acaso. O valor genético é próprio da população na qual os acasalamentos são realizados e, assim, não se pode falar em valor genético de um indivíduo sem especificar a população na qual ele foi avaliado.
definição teórica
O valor genético de um animal é igual à soma dos efeitos médios dos genes que ele possui, sendo a soma feita para todos os alelos de um locus e para todos os loci.É o mesmo que a soma dos efeitos independentes (efeitos aditivos) dos seus genes.Para um locus com dois alelos, o valor genético seria:

definição prática
O valor genético aditivo de um animal é igual a duas vezes o desvio médio do valor da progênie em relação à média da população, quando o referido animal é acasalado com um determinado número de indivíduos tomados ao acaso.
Combinações genéticas não aditivas fazem com que as definições teórica e prática não sejam equivalentes.
desvios de dominância
Considerando-se um locus com dois alelos, a diferença entre o valor genotípico (G) e o valor genético (A) para determinado genótipo, fornece o valor do desvio de dominância (D), ou seja, D = G - A.

desvios epistáticos (I)
Quando mais de um locus estão envolvidos, o valor genotípico pode conter um desvio adicional devido a combinações não aditivas entre os loci, combinações estas que constituem a epistasia.
A natureza complexa das interações não deve, todavia, ser motivo de preocupações porque no “valor genotípico agregado”, todas as interações são tratadas em conjunto, como um único desvio de interação (I).
G = A + D + I
Lembrar que A = VG e D + I = VCG.
variância
A genética dos caracteres quantitativos tem seu estudo centrado na variação. A ideia básica do estudo da variação é a sua partição em componentes atribuíveis a diferentes causas. A magnitude relativa desses componentes determina as propriedades genéticas da população, em particular, o grau de semelhança entre parentes. Será considerado aqui, a natureza desses componentes e como eles dependem das frequências gênicas.
componentes de variância
A quantidade de variação é medida e expressa como variância. Os componentes nos quais a variância é parcionada são os mesmos descritos anteriormente, quer dizer, P = G + E, sendo G = A + D + I. Portanto, P = A + D + I + E.
Os componentes de variância são, aqui, deduzidos em termos de frequência gênica e de valores genotípicos arbitrários (+a , d e -a). Considerando-se os valores expressos como desvio da média da população e que a interação genótipo x ambiente não está
incluída no modelo, tem-se:

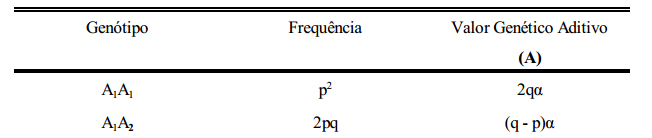
variância genética aditiva (VA)
É a variância dos valores genéticos aditivos da população. Considerando-se um locus com dois alelos, esses valores são:






4 Endogamia e parentesco I
conceituação
Endogamia é um sistema de acasalamentos no qual os animais envolvidos são mais aparentados entre si do que a média de parentesco da população como um todo. Entende-se por parentesco a relação existente entre indivíduos que tenham pelo menos um ancestral comum.
Entre os acasalamentos endogâmicos, também chamados de consanguíneos, podem-se citar os seguintes: a) progênie/ pai; b) progênie/ mãe; c) meio-irmãos; d) irmãos completos; e) primos f) tio/sobrinho.
Quando indivíduos aparentados se acasalam, a progênie tende a se tornar mais homozigota. Esse aumento de homozigose e consequente diminuição de heterozigose é a razão fundamental para as mudanças genotípicas associadas com a endogamia.
coeficiente de endogamia
Existem dois conceitos diferentes para este coeficiente:
a) Conceito de Malecot (1948) --> conceito probabilístico
b) Conceito de Wright (1952) --> conceito estatístico
coeficiente de endogamia segundo malécot
Malecot (1948) definiu coeficiente de endogamia (F) como a probabilidade de que dois alelos em um locus sejam idênticos por descendência, ou seja, venham de um mesmo ancestral comum.
O valor do coeficiente de endogamia (F) representa o provável aumento de homozigose resultante do acasalamento de indivíduos mais aparentados do que a média da população. F varia de 0 a 1, ou seja, de 0% a 100%. O grau de endogamia medido pelo F é relativo a uma dada população em um dado momento.
O aumento da homozigose expresso pelo F é o resultado mais provável, o que se espera em média. Muitos loci podem estar envolvidos e, ao acaso, maior ou menor proporção de loci podem se tornar homozigotos do que o valor F realmente indica. Mesmo que dois indivíduos em uma linha tenham o mesmo valor de F, eles podem não terem se tornado homozigotos para os mesmos loci. O que se espera é que a mesma proporção de loci tenha se tornado homozigota. Devem ser distinguidos os dois tipos de homozigose:
Autozigose ---> os indivíduos são homozigotos por descendência (os dois alelos provém de um mesmo ancestral).
Alozigose ---> Os indivíduos são homozigotos "em estado" (os dois alelos não provém de ancestral comum)

Assim,

Em que:
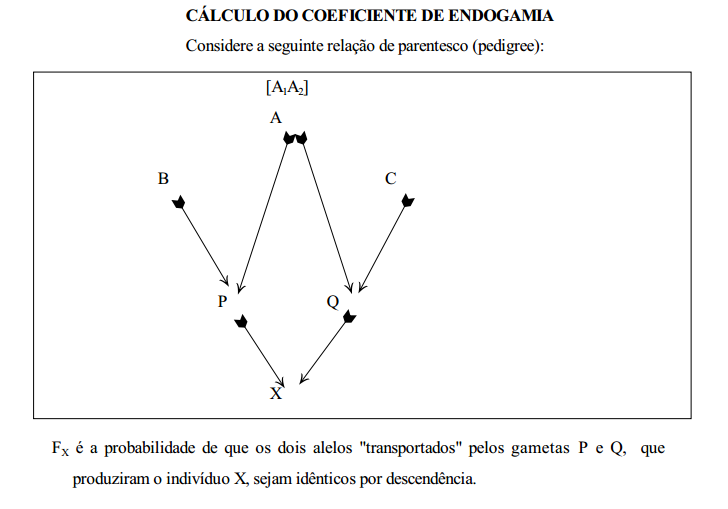
FX = Coeficiente de endogamia do indivíduo X
n1 = número de gerações que decorrem do pai até o ancestral comum (de P até A)
n2 = número de gerações que decorrem da mãe ao ancestral comum (de Q até A)
Deve-se, no entanto, considerar uma outra probabilidade: o ancestral A pode ser homozigoto por descendência, por endogamia prévia. Neste caso, X seria homozigoto mesmo se seu genótipo fosse A1A2 ou A2A1 (os dois genótipos sendo distinguidos conforme A1 venha por P ou por Q).
A probabilidade de que X seja A1A2 ou A2A1 1/16 + 1/16 = 1/8
A probabilidade de X "transportar" genes idênticos por descendência sendo seu genótipo A1A2 ou A2A1 é igual a 1/8FA, sendo que FA é o coeficiente de endogamia do ancestral comum A.

coeficiente de endogamia segundo wrightt
Wright (1952) conceitua o coeficiente de endogamia de um indivíduo X (FX) como a correlação entre os dois gametas em união.

parentesco
É a relação existente entre dois indivíduos que tenham pelo menos um ancestral comum. O parentesco é uma medida da proporção provável de genes que são idênticos, em dois indivíduos, devido ao ancestral comum (genes idênticos a mais que a população base). É baseado na probabilidade de que dois indivíduos sejam semelhantes em mais genes do que o seriam dois indivíduos retirados aleatoriamente da população.
A relação de parentesco mais simples é aquela entre progênie e um dos pais. Este grau de parentesco é fundamental para a determinação de outros graus. Considerando-se que a metade dos genes de um animal vem do pai e metade vem da mãe, um filho tem 50% de parentesco com o pai e 50% com a mãe. Um neto tem 25% de parentesco com cada um dos 4 avós e assim por diante.
Tendo em vista que um maior grau de parentesco deve refletir maior probabilidade de que dois indivíduos tenham os mesmos genes, o conhecimento desse grau de parentesco é útil na ponderação das informações dos parentes, quando se avalia o mérito genético de um indivíduo. Assim como para o coeficiente de endogamia, existem duas conceituações de coeficiente de parentesco: segundo Malecot (1948) e segundo Wright (1952).
coeficiente de parentesco segundo malécot
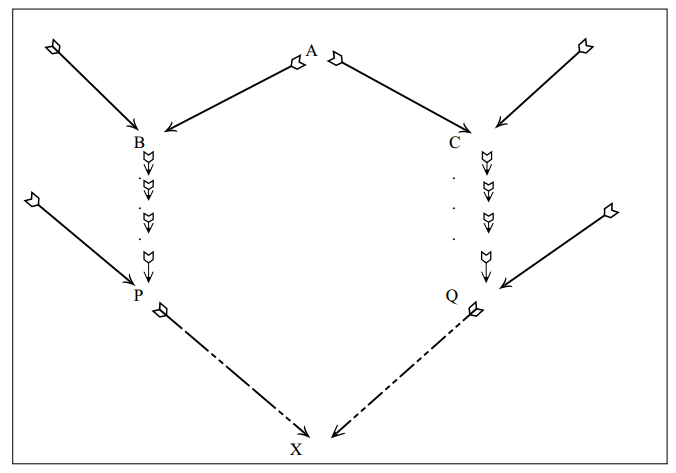
Malécot (1948) define o coeficiente de parentesco entre dois indivíduos, P e Q (fPQ) como a probabilidade de que um gene tomado ao acaso no indivíduo P seja idêntico por descendência a um gene tomado ao acaso no indivíduo Q. Considere o seguinte "pedigree":
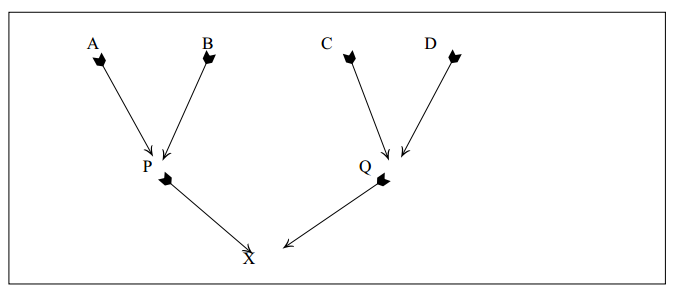
Tome um gameta ao acaso do animal P; repita isso várias vezes. Em 50% dos casos os gametas de P vão "transportar" genes de A e em 50% genes de B. Da mesma forma para os gametas do animal Q, metade terão genes de C e metade, genes de D. Assim, os dois gametas, um de P e outro de Q vão "transportar" genes de A e de C em 1/4 dos casos, de A e de D em 1/4, de B e de C em 1/4 , de B e de D em 1/4. Mas, a probabilidade de que dois genes tomados ao acaso, um de A e outro de C, sejam idênticos por descendência é igual ao coeficiente de parentesco de A com C (fAC). Da mesma forma, para A e D (fAD), B e C f(BC) e B e D (fBD), ou seja,
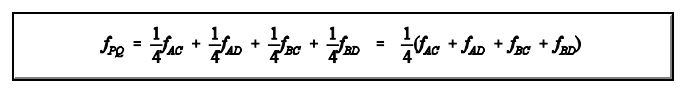
alguns parentescos fundamentais
Para o cálculo do coeficiente de parentesco pelo modelo acima, há necessidade de se conhecerem alguns parentescos básicos. São eles:
a) parentesco do indivíduo consigo mesmo
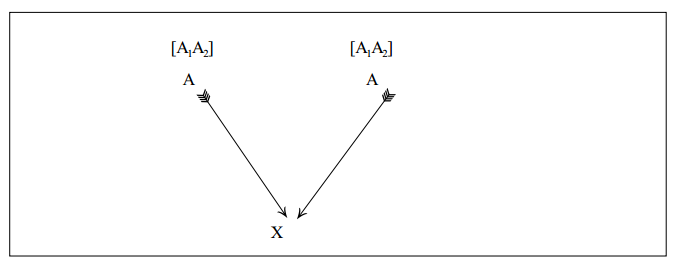
A probabilidade de que dois gametas tomados ao acaso no indivíduo X sejam ambos A1 é
igual a 1/4. A probabilidade de que sejam ambos A2 é 1/4. A probabilidade de que sejam ambos A1 ou ambos A2 é igual a 1/2. A probabilidade de que sejam A1 e A2 ou A2 e A1 é 1/2. A probabilidade de que A1 e A2 sejam idênticos por descendência é FA.
5 Endogamia e parentesco II

parentesco entre meio-irmãos
Considere o "pedigree" abaixo:
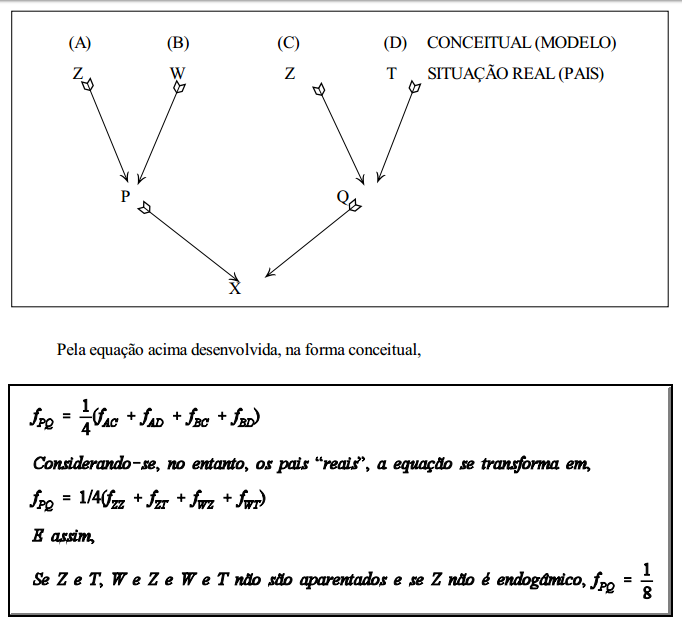
coeficiente de endogamia: parentesco de malécot
Note-se que, na página 127, para o mesmo pedigree, FX = 1/8, ou seja, o coeficiente de endogamia de um indivíduo X é igual coeficiente de parentesco entre seus pais (segundo o conceito de Malécot). Ou seja, FX = fPQ.
parentesco entre irmãos completos
Considere o "pedigree" abaixo,
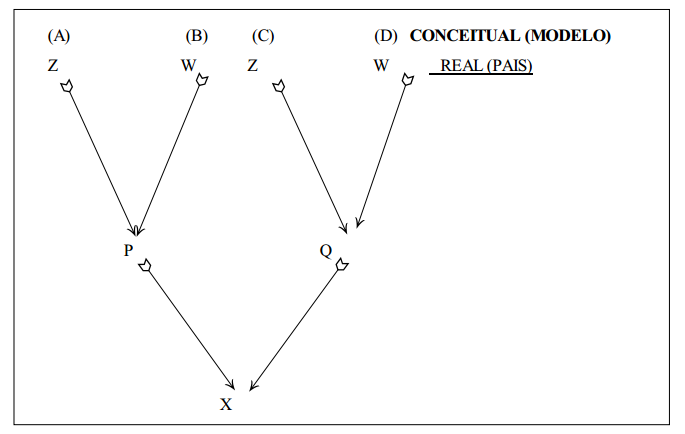
Para este pedigree acima,

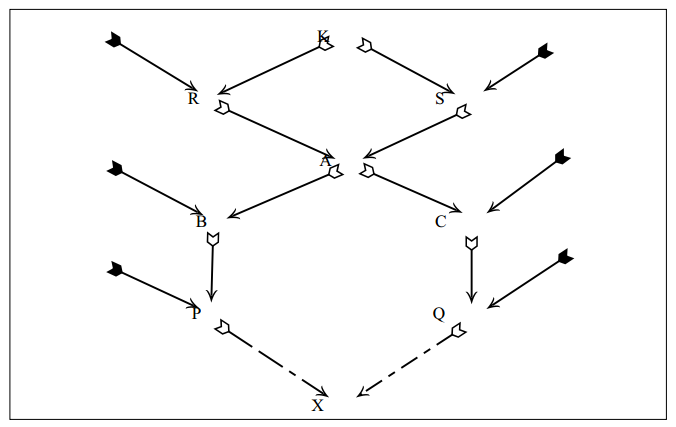
parentesco entre indivíduos de gerações diferentes
Se há sobreposição de gerações, pode-se ter a necessidade de calcular o parentesco entre indivíduos pertencentes a gerações diferentes. Considere o seguinte pedigree:
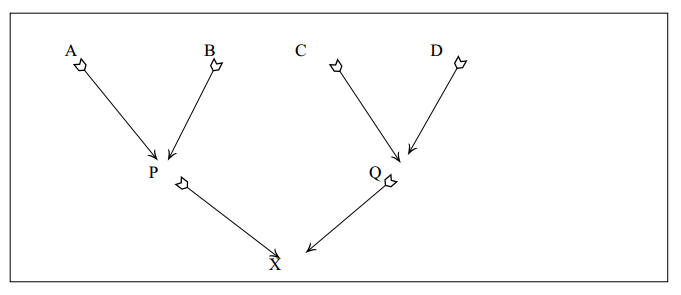
As expressões para o cálculo do parentesco entre P e C ou entre P e D ou Q e A ou Q e B podem ser deduzidas pelo seguinte raciocínio: Tome um gameta ao acaso de P; repita isso várias vezes. Em 50% dos casos os gametas de P vão "transportar" genes de A e em 50% genes de B. Agora, Tome um gameta ao acaso de C; repita isso várias vezes. Em 100% dos casos os gametas de C vão "transportar" genes de C. Assim, os dois gametas, um de P e outro de C vão "transportar" genes de A e de C em 1/2 dos casos, de B e de C em 1/2. Mas, a probabilidade de que dois genes tomados ao acaso, um de A e outro de C, sejam idênticos por descendência é igual ao coeficiente de parentesco de A com C (fAC). Da mesma forma, B e C f(BC), ou seja,
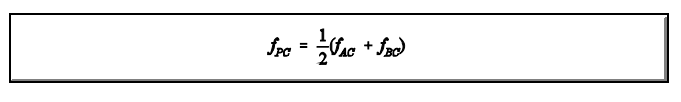

As expressões acima mostram que o parentesco entre dois indivíduos pertencentes a gerações diferentes é equivalente ao parentesco médio entre o indivíduo mais velho e os pais do mais novo.
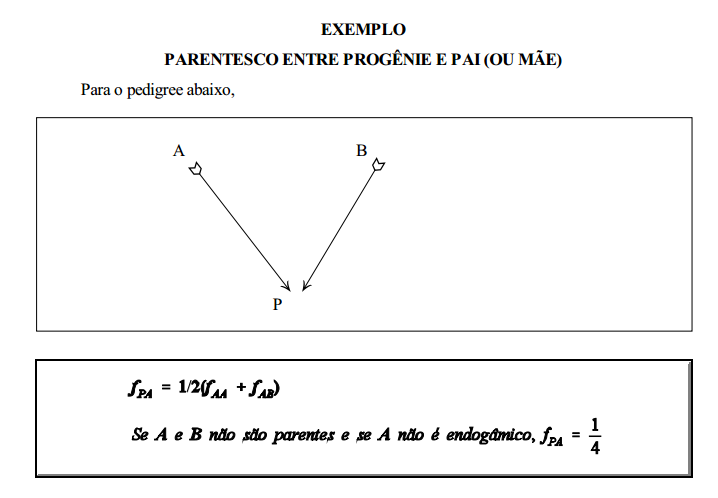

De acordo com esta última expressão, o parentesco entre dois indivíduos (em geral) é equivalente ao parentesco médio entre um deles e os pais do outro.
coeficiente de parentesco segundo wright
Segundo S.Wright (1952), o coeficiente de parentesco entre dois indivíduos P e Q (RPQ) é
o coeficiente de correlação entre os genótipos desses indivíduos, e pode ser expresso da seguinte forma:
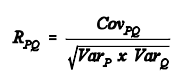
covariância genética( ou simplesmente parentesco de wright )
Se na expressão acima, RPQ é a correlação entre os genótipos, o seu numerador é a covariância entre esses mesmos genótipos e pode ser assumida como covariância genética aditiva entre os indivíduos P e Q. Esta covariância será sempre representada, neste material didático, como aPQ. A expressão para o cálculo de aPQ pode ser deduzida usando-se diagramas de passagem, da seguinte forma:
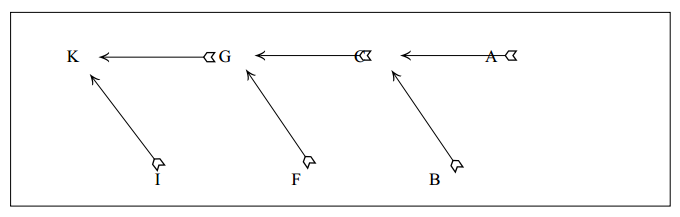
O indivíduo A transmite a metade de seus genes ao indivíduo C, então aAC = 1/2 = (1/2) ou seja, a probabilidade de que um determinado gene de A seja transmitido a C é 1/2. O animal C transmite a metade dos genes para G e aAG = 1/4 = (1/2) 2 = (1/2) 2 quer dizer, a probabilidade de que um determinado gene de A seja transmitido a G é 1/4 = (½) 2+0 .
Generalizando, para um pedigree qualquer (figura abaixo),

Se houver mais de um ancestral comum, como no pedigree abaixo,
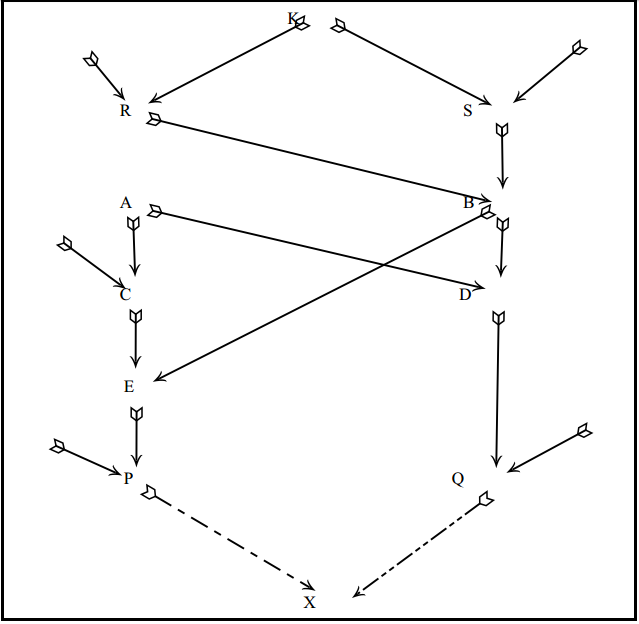
Então,
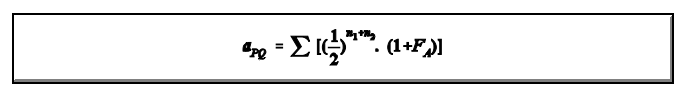
A covariância genética (aPQ), também chamada de parentesco, é a medida apropriada da fração de efeitos dos genes idênticos e é uma medida relativa da covariância entre os valores genéticos aditivos dos parentes. Assim, aPQ é usado na ponderação dos registros de produção dos parentes nos modernos métodos de avaliação genética.


A lógica da expressão de RPQ
Considerando-se que a endogamia aumenta a homozigose, um animal endogâmico irá
transmitir genes idênticos a cada um de seus descendentes de forma muito mais frequente do que um animal tomado ao acaso da população.
Se o ancestral comum a dois indivíduos é endogâmico, estes têm mais genes em comum e portanto são mais aparentados do que se o ancestral comum não fosse endogâmico. Para esta correção, a contribuição do ancestral comum é multiplicada por (1+ FA ).
A endogamia torna também a população mais variável pela produção de linhas endogâmicas separadas. Descendentes endogâmicos de qualquer animal terão maior porcentagem de homozigose do que os de um animal não endogâmico, mas podem ser homozigotos para diferentes alelos do mesmo par e assim menos aparentados do que se não fossem endogâmicos. O denominador da expressão de RPQ corrige para esta situação.
6 Cálculo da endogamia e do parentesco pelo método tabular
O método dos diagramas de passagem é prático para pequenos pedigrees, mas torna-se complicado se o número de animais aumentar muito.
O método tabular baseia-se no princípio de que se dois animais são parentes, um ou ambos os pais de um deles é também parente do outro do mesmo par. A grande vantagem deste método
é que, uma vez terminada a tabela, têm-se todas as covariâcias ou parentescos possíveis entre os animais e também o coeficiente de endogamia de cada um deles. Esta tabela, conhecida como "matriz de parentesco" é usada pelos programas computacionais de avaliação genética.
Na página 139 (cálculo do coeficiente de parentesco segundo Malécot), demonstrou-se que o parentesco entre dois indivíduos é equivalente ao parentesco médio de um deles com os pais do outro. O mesmo princípio é aplicado aqui.
Considerando-se o "pedigree" abaixo pode-se, por meio de regras simples, determinar o parentesco pela construção de uma tabela que inclui todos os indivíduos.
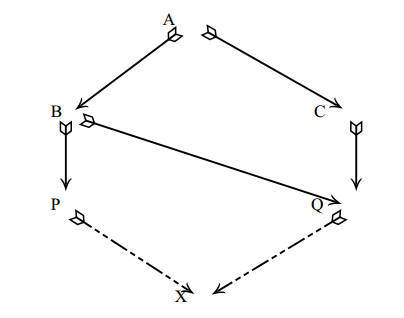
regras para computar os parentescos e os coeficientes de endogamia
1. Determinar quais os animais que serão incluídos na tabela. Ordená-los segundo a idade, primeiro os mais velhos.
2. Montar uma tabela com nomes ou números dos animais.
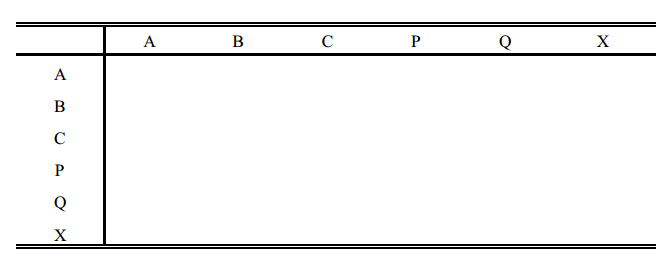
3. Escrever acima dos nomes (ou números) dos animais os nomes (ou números) dos seus pais. Se não forem conhecidos, colocar barras.
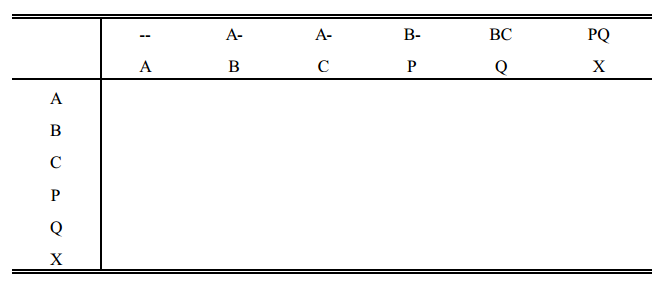
4. Colocar 1 em cada célula diagonal da tabela. 1 é o parentesco do animal consigo mesmo (na ausência de endogamia). Para os animais base, assumir que o parentesco é zero.
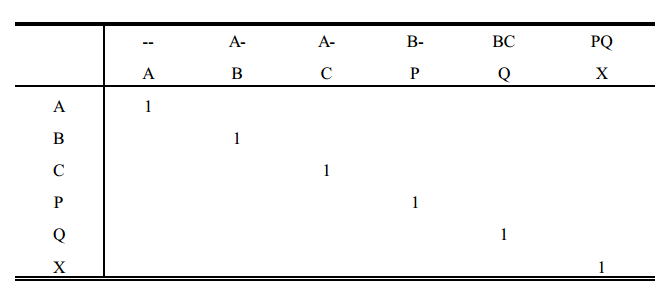
5. Computar cada célula fora da diagonal como a média dos valores nesta linha, correspondentes às colunas do pai e da mãe. Terminada cada linha, preencher a coluna correspondente com os valores dessa linha.


6. Adicionar, nas células da diagonal, a metade do parentesco entre os pais. O parentesco entre os pais pode ser obtido na tabela, na intersecção entre linha e coluna dos pais. A metade do parentesco entre os pais corresponde à endogamia do indivíduo da célula (rever teoria na página 143). Ou seja,


7. Repetir as regras 5 e 6 até completar a tabela, fazendo sempre uma linha por vez. Lembrar que:

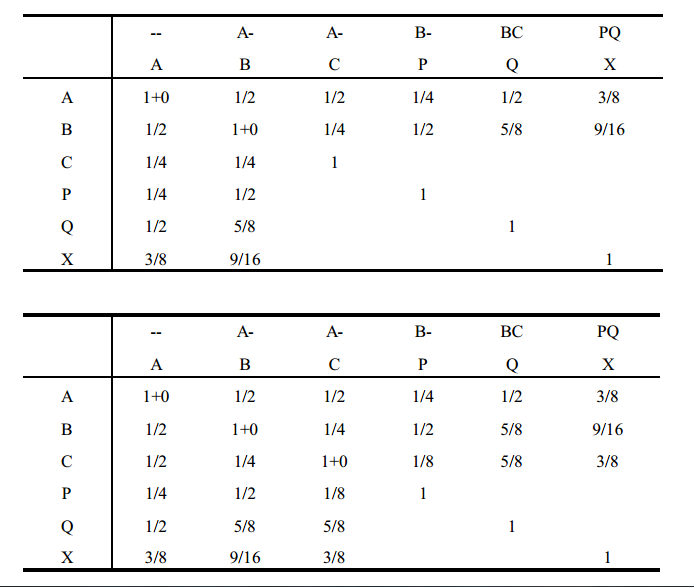
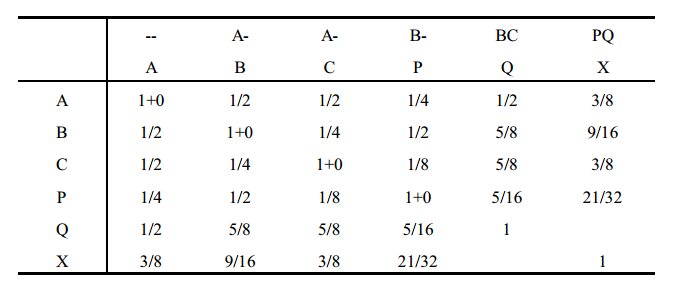

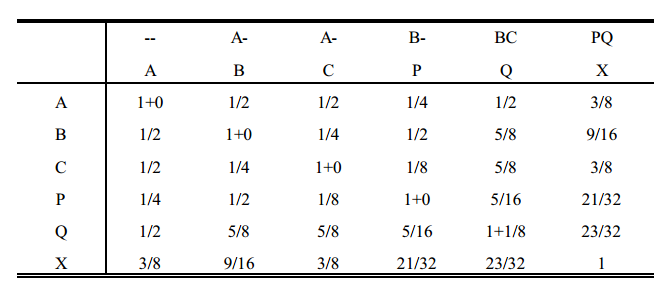
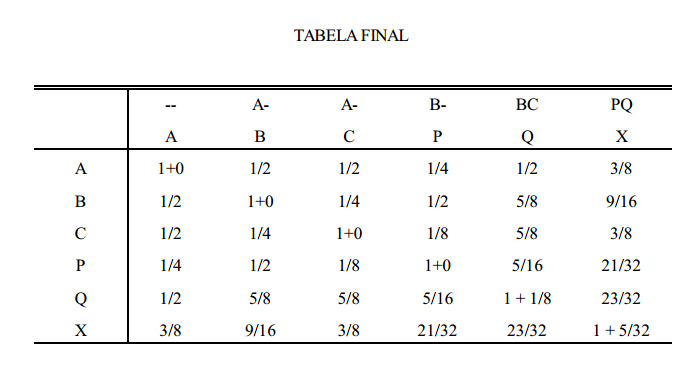
tabela de covariâncias genéticas ( parentesco de wright )
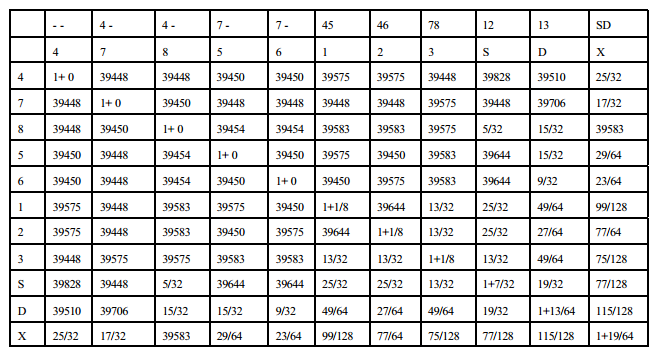
observações sobre a tabela acima
I - Os valores de cada célula fora da diagonal correspondem à covariância genética ou parentesco segundo Wright (aPQ)
II - Na diagonal, os dois valores precisam ser somados para corresponder à covariância genética (aPQ). O segundo termo dentro da célula da diagonal corresponde à endogamia do indivíduo (FX).
